植物共発現データベース「ATTED-II」がアップデート:収載植物種が19種20系統に拡張され、新たな種間比較解析ツールを実装
- その他
- ファンディング
- 統合化推進プログラム
2026年2月18日、東北大学 大学院情報科学研究科の大林 武 教授らは、植物の遺伝子共発現データベース「ATTED-II」をv13にアップデートし、共発現情報を収載する植物種を19種20系統に拡張するとともに、種をまたいだ共発現関係を比較する新たな解析ツールを実装しました。
近年、穀物や野菜などの実用植物を含むさまざまな植物種のゲノム解析が行われていますが、シロイヌナズナのようにこれまでよく研究されてきた「モデル植物」とは異なり、機能がわからない遺伝子が多数見つかってきます。特定の条件や環境下での発現に相関が見られる遺伝子群は、関係する一連の生理的機能を担っていることが多く、共発現情報は、それらの遺伝子の機能や遺伝子発現の制御関係の理解に役立つものと考えられています。
ATTED-IIは、2004年に植物の共発現情報を収載したデータベースとしてはじめて公開されました。前回の2024年9月のv12へのアップデートでは、植物種が11種に拡張されるとともに、共発現する遺伝子の主成分(Principal component、以下PC)分析から着目する2つの遺伝子が共発現する条件や環境を調べることができる「PC View」と、着目する2つの遺伝子の発現パターンの相関図を可視化する「CoexViewer」が実装されました。
今回のATTED-II v13へのアップデートでは、植物種が19種20系統にまで拡張されるとともに、新たな種間比較解析ツールが実装され、異なる種間の共発現遺伝子の比較や、それらが担う生理的機能のさらなる考察ができるようになりました。大量のサンプルの主成分分析によるサンプル環境を表示する「PC View」が高機能化され、各主成分軸に関連するサンプルリストや遺伝子リストを表示するのみならず、要約を提供することで複数の主成分軸の違いを検討しやすくなりました。具体的には、遺伝子リストについてはKEGG濃縮検定の結果を提供し、その結果と変動サンプルをLLMを用いて3段階の粒度で要約した情報(ラベル・短い要約・長い要約)が提供されるようになっています。ラベルと短い要約については、遺伝子ペアの共発現を表示する「Coex Viewer」上でも表示することで、共発現条件の理解を支援する機能が新たに追加されました。さらに、共発現情報の種間比較機能が高度化され、葉緑体や細胞核といった細胞内局在別の共発現マップを表示することにより、遠縁種間での共発現遺伝子の類似性や相違点を比較解析できるようになりました。
ATTED-IIは、JST統合化推進プログラムの研究開発課題「非モデル植物のための遺伝子ネットワーク情報活用基盤」(研究代表者 大林 武 東北大学 大学院情報科学研究科 教授)の一環で開発・提供しています。
ATTED-II v13に共発現情報が収載されている植物種 (19種20系統)
<双子葉植物>
- シロイヌナズナ標準種(Arabidopsis; 学名 Arabidopsis thaliana; 記号 ath-r)
- シロイヌナズナ非標準種(Arabidopsis; 学名 Arabidopsis thaliana; 記号 ath-e)
- トマト(Tomato; 学名 Solanum lycopersicum; 記号 sly)
- タルウマゴヤシ(Medicago; 学名 Medicago truncatula; 記号 mtr)
- ダイズ(Soybean; 学名 Glycine max; 記号 gma)
- ポプラ(Poplar; 学名 Populus trichocarpa; 記号 ppo)
- ブドウ(Grape; 学名 Vitis vinifera; 記号 vvi)
- セイヨウアブラナ(Field mustard; 学名 Brassica napus; 記号 bna)**
- アプランドワタ(Upland cotton; 学名 Gossypium hirsutum; 記号 ghi)**
- ジャガイモ(Potato; 学名; Solanum tuberosum; 記号 sot)**
- タバコ(Tobacco; 学名; Nicotiana tabacum; 記号 nta)**
- オレンジ(Orange; 学名 Citrus sinensis; 記号 cit)**
<単子葉植物>
- コメ ジャポニカ米(Rice; 学名 Oryza sativa subsp. japonica; 記号 osa-r)
- コメ インディカ米(Rice; 学名 Oryza sativa subsp. indica; 記号 osa-e)**
- トウモロコシ(Maize; 学名 Zea mays; 記号 zma)
- コムギ(Wheat; 学名 Triticum aestivum; 記号 tae)*
- オオムギ(Barley; 学名 Hordeum vulgare; 記号 hvu)*
- タカキビ(Sorghum; 学名 Sorghum bicolor; 記号 sbi)**
- ミナトカモジグサ(Brachypodium; 学名 Brachypodium distachyon; 記号 bdi)**
<緑藻類>
- クラミドモナス(Chlamydomonas; 学名 Chlamydomonas reinhardtii; 記号 cre)**
* :v12で新たに共発現情報が収載された植物種(2024年9月)
** :v13で新たに共発現情報が収載された植物種・系統(2026年2月)

図1 ATTED-II v13のトップページ
ATTED-II v13.0のトップページ。GeneTable、EdgeAnnotation、CoExSearchなどの検索機能(Search)とNetworkDrawer、CoexMap、Hclusterなどの解析機能へのリンク(Draw)のほか、収載されている19種20系統の植物ごとの主なサンプルページへのリンク(Target species with page examples)やダウンロードページ(Bulk download)へのリンクがある。
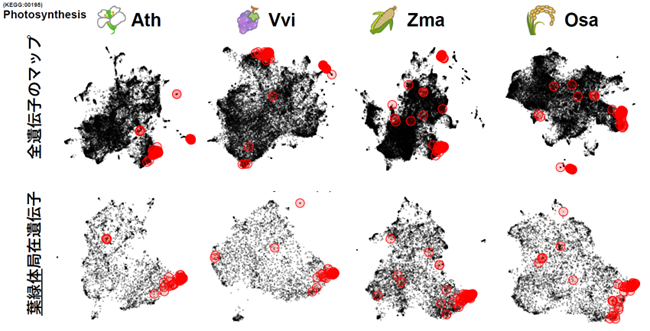
(A) 葉緑体に局在する光合成関連遺伝子
(B) 細胞核に局在するリボソーム生合成関連遺伝子
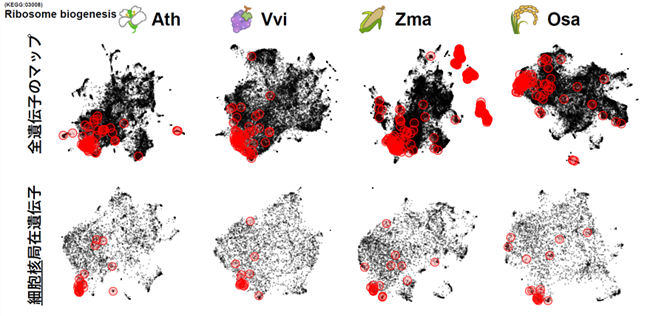
図2 新たに実装された種をまたいだ共発現関係を比較する解析ツール
(オルガネラ単位でのCoex Viewer)
(A) 葉緑体で共発現する遺伝子の植物種間比較。左から、シロイヌナズナ(Ath)、ブドウ(Vvi)、トウモロコシ(Zma)、コメ(Osa)。上段は全遺伝子での共発現遺伝子マップ、下段は葉緑体に局在するタンパク質の遺伝子の共発現マップ。赤丸は光合成関連遺伝子(KEGG:00195)を示す。全遺伝子で見ると光合成関連遺伝子(KEGG:00195)の局在に一貫性が見られなかったが、葉緑体局在に着目すると種間で一貫した配置を示した。
(B) 細胞核で共発現する遺伝子の植物間比較。左から、シロイヌナズナ(Ath)、ブドウ(Vvi)、トウモロコシ(Zma)、コメ(Osa)。上段は全遺伝子での共発現遺伝子マップ、下段は細胞核に局在するタンパク質の遺伝子の共発現マップ。赤丸はリボソーム生合成関連遺伝子(KEGG:03008)を示す。全遺伝子で見るとリボソーム生合成関連遺伝子(KEGG:03008)の局在に一貫性が見られなかったが、細胞核局在に着目すると種間で一貫した配置を示した。
関連リンク
- ATTED-II
- 非モデル植物のための遺伝子ネットワーク情報活用基盤 - 採択課題 | NBDCサイト
課題概要や報告書などを掲載しています。