日本人はお酒に弱いというのは本当か? ~TogoVarを使って、日本人とその他の集団のバリアント頻度を比較する~
NBDCの豊岡です。
本年も12月を迎えましたが、皆様どのような一年を過ごされたでしょうか。
年末年始はその季節特有の料理を食べる機会も増えると思いますので、各食材のゲノムが解読されているかをGenomeBentoProject(用語解説①)のページで見ながら料理を味わうのも、一つの楽しみかもしれません。
今回の記事ではアルコール分解能力に関連するバリアント(ゲノム配列の個人による違い)の説明を糸口に、様々なデータベースの紹介と、併せて当センターのサービスであるTogoVarの紹介もしていきたいと思います。
1.お酒の強さは何で決まるのか
さて、世間ではよく「日本人にはお酒に弱い人が多い」といったことが言われます。これは本当でしょうか?
みなさんが飲酒などでアルコールを体に摂取すると、大部分は

と2段階で分解されます。
この途中で生じるアセトアルデヒドがうまく分解されないと、顔が赤くなったり二日酔いになったりする原因になるのです。
「アセトアルデヒド → 酢酸」の分解に関わる酵素はALDH(アルデヒド脱水素酵素)と呼ばれており、複数のアイソフォーム(機能はほとんど同じだがアミノ酸配列が異なるタンパク質)が存在します。
そして、アイソフォームの一つであるALDH2について、これをコードする遺伝子上に存在するバリアントrs671が、アルデヒドを分解する能力に大きく影響することが多くの研究で報告されています。
(rs番号について詳しく知りたい方は用語解説②をご覧ください)
このrs671については、標準的な遺伝子配列と同じ塩基配列(12番染色体の112241766番目の塩基が"G")を持つ人はアセトアルデヒドの分解能力が高く、標準的な遺伝子配列と異なる塩基配列(前述の塩基が"A")を持つ人は分解能力が低いとされ、日本を含む東アジアの集団では後者の塩基配列を持つ人の割合が多いといわれています。(参考文献 1)
では、本当に日本人とその他の集団でバリアントの頻度に差があるのか、様々な研究プロジェクトで作られているデータベースを確認してみましょう。
2.ヒトゲノムのバリアントデータベースを調べてみる
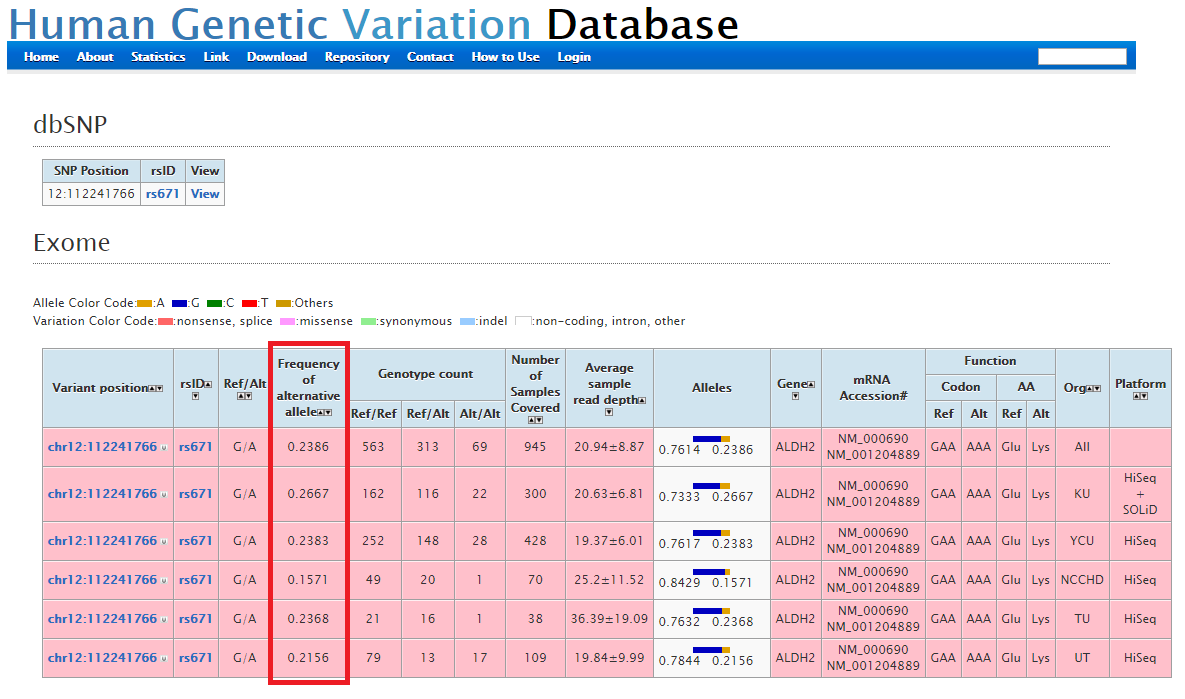
京都大学が運営する、日本人ゲノム中のバリアント情報を収集したHGVDでは、rs671は15-26%程度の出現頻度を示しています。(下図赤枠)(参考文献 2,3)
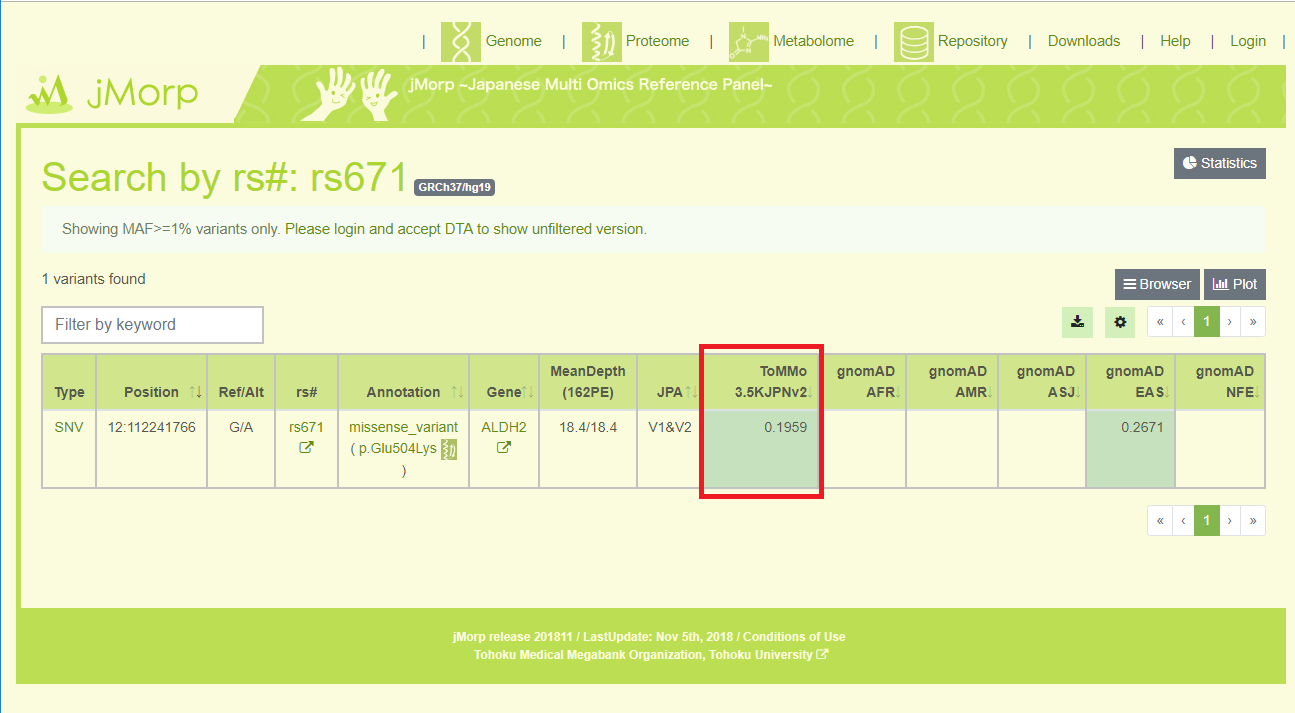
また、東北メディカル・メガバンク機構が運営するiJGVDや、jMorpでは、20%程度の出現頻度を示しています。(下図赤枠)(参考文献 4)
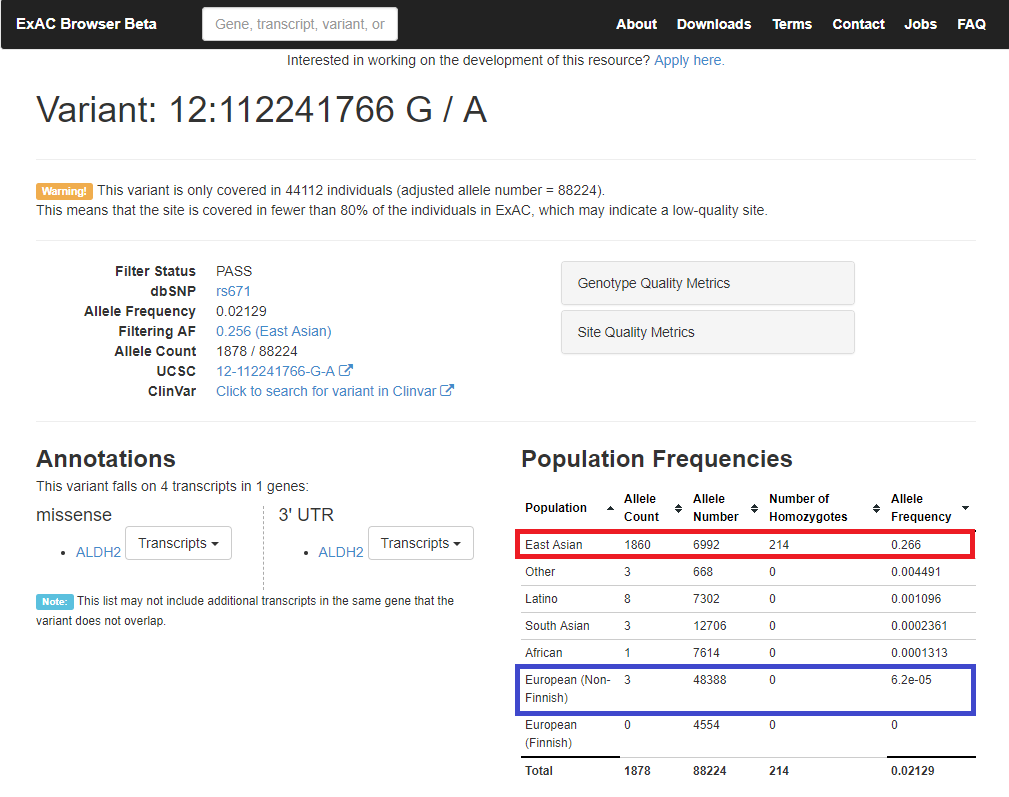
さらに、米国Broad研究所が運営するExACでも、「East Asian」集団では約26%の出現頻度を示しています。(下図赤枠)(参考文献 5)
一方、ExACでその他の集団を見ると、出現頻度ははるかに低い数字となっています。(例えば、「European (Non-Finnish)」集団における、出現頻度は0.006%前後です)(上図青枠)
やはり、その他の集団と比べて日本人には、「アルデヒドを分解する能力が低い≒お酒に弱い」人が多いようです。
3.TogoVarを使ってバリアントの情報を効率的に集める
疾患とバリアントの関係を研究している研究者は、公開されているデータベースをいろいろと回りながら、前章のような情報収集をいつも行っています。
NBDCでは、これらの散在している情報をワンストップで調べることができるTogoVarというサービスを本年6月に公開しました。前述したような、いろいろなデータベースを回って収集していた情報を、このサイトでは一括して集めることが可能です。
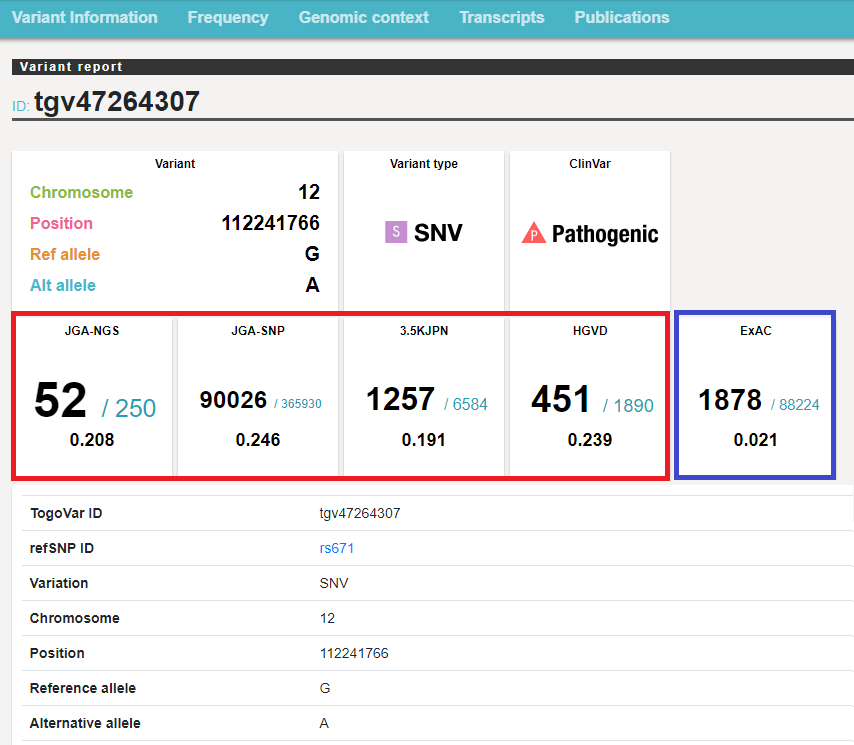
TogoVarのトップページにアクセスし、検索窓に「rs671」と入力して検索するだけで、該当するバリアントの概要を見つけることができます。より詳しい情報が必要であれば、IDをクリックすることで詳細ページに進むことができます。(下図)
ここまでrs671について述べてきましたが、アルコール分解過程のうち「アルコール → アセトアルデヒド」の段階についても、分解に関わる酵素としてADH(アルコール脱水素酵素)のアイソフォームの一つであるADH1Bが知られており、その分解能力に関わるバリアントとしてrs1229984が報告されています。
このバリアントの頻度情報を集めるために、再度前記のデータベースを回って情報を集めるのは大変手間がかかりますが、TogoVarではすぐに調べることができます。
ぜひ一度、お試しください。
また、TogoVarの使い方については、統合TVでも公開していますし、同じ動画をYouTubeにも公開していますのでご覧ください。
一方、バリアントの情報を収集するためにはTogoVarだけ確認すればよいというものではなく、各データベースを運営しているプロジェクトごとに、提供している情報は様々な特色があります。まずは、TogoVarを通じてヒトゲノムのバリアントのデータベースに様々なものがあることを知っていただき、それから各データベースの特徴を順次把握されると良いかと思います。
4.TogoVarの説明をもう少し
TogoVarは、HGVD、iJGVD、ExAC、ClinVarから情報を収集していますが、その他に当センター独自のデータベースであるJGA-SNPとJGA-NGSの情報も取り込んでいます。これらは当センターが運営しているNBDCヒトデータベースのデータをもとに作成しており、順次サンプル数を増やしていく予定です。
このNBDCヒトデータベースでは、寄託されたヒトゲノムデータを他の研究者が利用することが可能ですので、日本人のゲノムデータをお探しの方はぜひご利用を検討ください。
最後になりましたが、rs671のバリアントに該当しないからといって(筆者のように)お酒を飲み過ぎることの無いように、くれぐれも良いお年をお迎えください。
用語解説
① GenomeBentoProjectのサイト(http://wiki.lifesciencedb.jp/mw/GenomeBentoProject)には、ゲノム研究に関わる有志の方々が手弁当で集めた、ゲノム配列が決定している身近な食材の情報が掲載されています。
(来年の3月ぐらいに情報が更新される、といううわさも聞きました)
② rs番号は、様々な研究から報告されたヒトゲノム中のバリアントを識別するために米国NCBIが付与しているもので、dbSNP(https://www.ncbi.nlm.nih.gov/snp/)というデータベースで参照することができます。この番号はdbSNPに登録された順に付与されているため、遺伝子上で隣り合うバリアントの番号が大きく異なることがあるのでご注意ください。
また、dbSNPでは長さが50bp以下のバリアントにrs番号を付与しており、それ以上の長さのバリアントについては別のdbVar(https://www.ncbi.nlm.nih.gov/dbvar/)で管理をしています。
さらに、バリアントと疾患との関連を臨床現場でも使えるように作られたデータベースが、同じく米国NCBIの運営するClinVar(https://www.ncbi.nlm.nih.gov/clinvar/)です。先ほどのrs671を調べると、"Susceptibility to hangover"や"Acute alcohol sensitivity"と関連することが、報告した論文の情報等とともにまとめられています。このデータベースは毎月最新の情報に更新されていますが、臨床現場における遺伝子解析の普及に伴い、この疾患とバリアントの関連を示す情報も今後さらに増加することが予想されます。
参考文献
- F. Takeuchi et. al., "Confirmation of ALDH2 as a Major locus of drinking behavior and of its variants regulating multiple metabolic phenotypes in a Japanese population". Circ J. 2011, 75(4):911-8. doi: 10.1253/circj.CJ-10-0774
- K. Higasa et al. "Human genetic variation database, a reference database of genetic variations in the Japanese population". J Hum Genet. 61:547-553, 2016. doi: 10.1038/jhg.2016.12
- M. Narahara et al. "Large-Scale East-Asian eQTL Mapping Reveals Novel Candidate Genes for LD Mapping and the Genomic Landscape of Transcriptional Effects of Sequence Variants". PLOS ONE. 2014, 9(6):e100924. doi: 10.1371/journal.pone.0100924
- Tadaka et al., "jMorp: Japanese Multi Omics Reference Panel". Nucleic Acids Research. 2018, Jan 4;46(D1):D551-D557. doi: 10.1093/nar/gkx978
- Monkol Lek et al. "Analysis of protein-coding genetic variation in 60,706 humans". bioRxiv. October 30, 2015. doi: 10.1101/030338
著者紹介
豊岡 理人(とよおか りひと)
システムエンジニア等を経て現在NBDC研究員。ヒトデータベース関連のサービスを担当。ヒトゲノムデータの再利用を促進中。趣味は城巡りとサッカー。